Deriva genética
| ||||||||
Deriva genética. Fluctuación aleatoria de las frecuencias alélicas como consecuencia del tamaño poblacional finito. La magnitud del cambio en la frecuencia alélica debido a la deriva genética está relacionada de manera inversa con el tamaño de la población.
La deriva genética junto con la selección natural son los dos mecanismos más importantes de sustitución alélica.
El modelo de Hardy-Weinberg supone el apareamiento al azar en poblaciones de tamaño infinito. Puesto que las poblaciones naturales tienen un tamaño finito, en cada generación hay un muestreo al azar de las gametas para formar la generación siguiente. Esto hace que las frecuencias de los alelos fluctúen de generación en generación. En consecuencia,
- Aparecen efectos de muestreo de una generación a la siguiente
- Ocurre evolución (cambio en la composición genética de la población)
- Los cambios en la frecuencia alélica ocurren al azar y no son adaptativos
Este proceso puede asimilarse a la extracción de una muestra finita de bolas de distintos colores de una urna: considere una urna que contiene un millón de bolas de diez colores diferentes. Si se extrae una muestra al azar de 500 000 bolas casi con toda seguridad la muestra contiene todas las bolas en una proporción muy similar a las proporciones originales. Sin embargo, si se extraen solo 5 bolas, seguramente la muestra será sesgada (no se pueden haber extraído más de 5 de los 10 colores- cualquier duplicación de color va a disminuir el número de colores-. Aún cuando se extraiga una muestra de 50, es poco probable que se mantengan las proporciones del millón original, el pequeño tamaño de la muestra impide la extracción de una muestra representativa. Si consideramos una población con un locus con dos alelos con frecuencias p y q, los individuos producirán muchas gametas en estas proporciones, pero sólo unas pocas formarán cigotas. Cuanto menor sea el número de cigotas o, lo que es lo mismo, el tamaño de la población, mayor será la probabilidad de que las frecuencias alélicas se desvíen de p y q.[1]
Cuando se pierde un alelo y todos los miembros de la población son homocigotas para el otro, se dice que el segundo alelo se ha fijado y su frecuencia es 100% o 1.
Como la deriva genética es un fenómeno aleatorio, diferentes poblaciones pueden derivar de modo distinto, aunque al principio del proceso tengan el mismo tamaño poblacional y las mismas frecuencias alélicas.
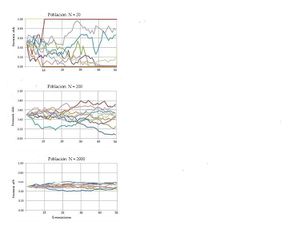
Estudios de simulación en computadora dan una idea del efecto de la deriva en las poblaciones. Se observan:
- Fluctuaciones más marcadas en las poblaciones pequeñas que en las grandes
- Reducción de la variabilidad en el tiempo
- Pérdida de toda la variación (se fija o se pierde un alelo)
- Divergencia genética entre poblaciones
- Mantenimiento de la frecuencia alélica promedio constante
La frecuencia de un alelo en una generación pasa a ser la probabilidad de obtener el alelo en la siguiente generación. Si la frecuencia de un alelo en una generación cambia, por ejemplo de 0.5 a 0.6, la probabilidad de obtener el alelo en la siguiente generación se hace 0.6 (60 %). Así, los cambios en las frecuencias alélicas se hacen acumulativos a través de las generaciones. Sin embargo, como los cambios en la dirección son al azar, un alelo que ha aumentado de frecuencia en una generación puede, en la siguiente generación, aumentar nuevamente o disminuir con igual probabilidad.
El proceso no continúa indefinidamente, sino que se detiene en una de dos situaciones: o bien cuando el alelo se fija (esto es, llega a ser el 100% de la población) o bien cuando se extingue (deja de existir, o sea llega a una frecuencia de 0). Cuando esto sucede, el alelo no puede cambiar de frecuencia a menos que aparezca un nuevo alelo por mutación. El resultado de la deriva suele ser la pérdida de variabilidad genética (disminuye la heterocigosidad y aumenta la homocigosidad), siendo un proceso que contrarresta la entrada de variabilidad genética por mutaciones y que conduce a la fijación o eliminación de uno de los alelos de la población.
La deriva también afecta la probabilidad de supervivencia de las nuevas mutaciones. La probabilidad de fijación de un alelo (esto es, llegar a ser el 100% de la población) es igual a su frecuencia en la población. Es decir, un alelo con una frecuencia de 0.99 tiene una probabilidad de fijación del 99% (1% de ser eliminado), uno con una frecuencia de 0.50 del 50% (50% de ser eliminado) y uno con una frecuencia de 0.01 del 1% (99% de ser eliminado).
Los tres resultados de la deriva (cambio en la frecuencia alélica, pérdida de variación dentro de la población y divergencia genética entre poblaciones) suceden de manera simultánea y todos son consecuencia del error de muestro-discrepancias aleatorias entre lo esperado teóricamente y los resultados reales obtenidos- . Los dos primeros resultados se producen dentro de las poblaciones, mientras que el tercero se presenta entre poblaciones.
Sumario
Casos extremos de deriva genética
La variación genética es la materia prima a partir de la cual, por selección natural, las diversas poblaciones de una especie se adaptan a los cambios en su medio ambiente. Nuevas variaciones genéticas surgen en el seno de las poblaciones a partir de las mutaciones o por inmigración de individuos de poblaciones distintas genéticamente. El número y abundancia relativa de los alelos en una población es una medida de su variación genética.[2]
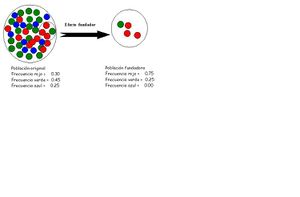
Dos casos especiales de deriva genética, conocidos como efecto fundador y cuello de botella genética ilustran las consecuencias de un tamaño de población reducido en las frecuencias de alelos de una especie.
Efecto fundador
Una consecuencia extrema de la deriva genética es lo que Ernst Mayr[3] denominó efecto fundador; éste se debe al establecimiento de una nueva población a partir de unos pocos individuos fundadores que portan sólo una pequeña parte de la variación genética total de la población parental. Como consecuencia de ello, los únicos alelos presentes en los descendientes son los que portaban los individuos fundadores.
La deriva genética es el resultado del muestreo de la población de origen, y una cierta cantidad de generaciones durante las cuales el tamaño de la nueva población permanece reducido. Este pequeño tamaño poblacional implica que la colonia puede tener:
- Poca variación genética, respecto a la población original
- Una muestra no aleatoria de los genes de la población original
Las poblaciones de muchas especies que viven en las islas oceánicas, aunque en la actualidad pueden constar de poblaciones con gran cantidad de individuos, son descendientes de uno o muy pocos colonizadores que llegaron por dispersión accidental. La situación es similar en otros sistemas ecológicos aislados.
El efecto fundador no solo puede eliminar algunos alelos, sino que también puede incrementar la frecuencia de alelos raros, en algunos casos relacionados con enfermedades genéticas, que así pueden pasar a estar representadas en una proporción mayor en el acervo génico.
Por ejemplo, la alta incidencia de la enfermedad de Huntington en los pueblos cercanos al lago Maracaibo en Venezuela. La enfermedad de Huntington, una enfermedad degenerativa del sistema nervioso, es causada por un alelo dominante. Al tratarse del alelo dominante, los individuos que tengan únicamente un progenitor con la enfermedad de Huntington tienen una probabilidad del 50% de padecer la enfermedad. En la población venezolana con enfermedad de Huntington, el alelo mutante llegó a principios del siglo XIX. Casi todos los individuos afectados pueden trazar su ascendencia hasta una mujer, María Concepción Soto. Soto tuvo diez hijos y se convirtió en la fundadora de una población de más de 18 000 personas.[4]
La deriva genética puede contribuir a la especiación. En el modelo de especiación peripátrida o por efecto fundador una pequeña población aislada diverge, por deriva genética, de la población de mayor tamaño de la cual se originó. La deriva genética y, tal vez, unas fuertes presiones selectivas causarían un cambio genético rápido en la pequeña población. Después de varias generaciones los individuos de la nueva población quedan aislados reproductivamente de los individuos de la población de origen. Por ejemplo la especiación por numerosas migraciones entre islas y efecto fundador en las moscas Drosophila del archipiélago hawaiano.
Cuello de botella genético
Un cuello de botella es un proceso demográfico que sufre una población cuando experimenta una drástica reducción del tamaño, ya sea por causas naturales o por causas antrópicas. Los principales efectos genéticos de un cuello de botella son la pérdida de variabilidad genética y el aumento de la consanguinidad, disminuyendo la capacidad adaptativa de la población y aumentando el riesgo de extinción de la especie. La pérdida de variabilidad genética que acompaña al evento de cuello de botella tiene aspectos cualitativos y cuantitativos. Cualitativamente pueden perderse alelos específicos y es poco probable que, mientras la población permanece pequeña, aparezcan de nuevo por mutación. Cuantitativamente, se reduce la variabilidad de rasgos específicos.
Muchas de las poblaciones que se encuentran en peligro de extinción sufrieron cuellos de botella genéticos, porque la actividad humana fraccionó, destruyó o deterioró su hábitat, provocando una reducción muy grande del número de individuos en poco tiempo. Los actuales programas de conservación se encuentran con dos problemas: quedan muy pocos individuos y su variabilidad genética es muy baja. Esto lleva a la aparición de enfermedades genéticas, a infertilidad y a una alta mortalidad de los juveniles. A esto se llama depresión endogámica.[5]
El efecto de la deriva durante el cuello de botella permanece durante varias generaciones, aún cuando las poblaciones han recuperado su tamaño original.
El elefante marino del norte (Mirounga angustirostrus) está geográficamente aislado del elefante marino del sur (Mirounga leonina). Los elefantes marinos del norte tienen poca variabilidad genética. Aparentemente, este extremo monomorfismo -virtualmente todos los individuos poseen un solo alelo en los 24 loci analizados- refleja la historia natural de la especie y es consecuencia de un cuello de botella poblacional. En el siglo XIX los elefantes marinos del norte fueron cazados para obtener su grasa y sus poblaciones quedaron al borde de la extinción. Los resultados de Hoelzel y colaboradores[6] indican un cuello de botella de tan solo 30 individuos con una duración de 20 años, o si la caza constituyo la principal presión en la población, un cuello de botella de menos de 20 individuos durante un solo año. Desde entonces, la población ha aumentado hasta más de 30 000 individuos, pero sus genes todavía llevan las señales de ese cuello de botella, su variabilidad genética es mucho menor que la de la población de elefantes marinos del sur que presenta una variación genética similar a la de otros grandes mamíferos.
Tamaño poblacional efectivo
En poblaciones reales, donde el número de individuos que se reproducen, transmitiendo sus genes a la siguiente generación, es finito se introduce el concepto de tamaño poblacional efectivo. El tamaño poblacional efectivo representa el número de individuos de una población ideal teórica (de fecundación externa, de tamaño constante y sin diferencias individuales en fecundidad) en que la tasa de cambio por deriva, medida en función de la tasa de pérdida de heterocigosidad, es la misma que la observada en la población real. El tamaño efectivo se designa como Ne, para distinguirlo del tamaño real, N. El tamaño poblacional efectivo cuantifica la tasa a la cual la variabilidad genética es erosionada por la deriva genética. La relación Ne/N es una medida que indica la desviación de la población real de la idealizada.
El tamaño poblacional efectivo (Ne) es un parámetro clave en conservación de poblaciones ya que el aumento de la consanguinidad es inversamente proporcional al tamaño efectivo de la población. La consanguinidad tiene varios efectos, pero el más importante y del cual derivan todos los otros es un aumento en la homocigosis.
El tamaño poblacional efectivo es especialmente sensible a la diferencia en el número de hembras reproductivamente activas respecto al número de machos. Cuando en una población hay diferente número de cada sexo, el tamaño efectivo de la población (Ne) puede ser estimado mediante la expresión: Ne = (4 NmNh)/ ( Nm+ Nh), donde Nm y Nh indican el número de machos y de hembras, respectivamente. Ne disminuye por desviaciones de una proporción igual de sexos. El elefante marino (Mirounga) es una especie políginica y la estructura unitaria de reproducción es el harén. Los harenes de los elefantes marinos del norte están formados por un macho y hasta 50 hembras.[7] Por lo tanto, el tamaño poblacional efectivo es de sólo 4 individuos y la relación entre el tamaño poblacional efectivo y el tamaño real de la población (Ne/N) es igual a 0.08. Este sistema social es un factor adicional que contribuye al alto grado de homocigosis encontrado en este elefante marino.
Otros factores adicionales que determinan el Ne incluyen:
Variación en el número de descendientes producidos por hembras, machos, o ambos: Cuando esta condición no se cumple, por ejemplo, cuando la progenie de unas pocas familias es notoriamente mayor, Ne disminuye.
Fluctuación del tamaño poblacional: La mayoría de las estimaciones de Ne se basan en que la población permanece estable en el tiempo, sin embargo, cuando existe variación cíclica a través del tiempo que afecta los tamaños demográficos, el tamaño poblacional efectivo a largo plazo también se ve afectado. La tasa de cambio por deriva aumenta durante los periodos de tamaño poblacional pequeño; de hecho, a largo plazo, el tamaño efectivo se ve más influido por los tamaños poblacionales más pequeños que por los más grandes.
Teoría neutralista
El neutralismo propone que la mutación genética y la deriva genética al azar, son las fuerzas fundamentales en el proceso de cambio a nivel molecular. De acuerdo a esta visión, a nivel molecular el aumento o disminución de determinados alelos en la población se debería exclusivamente al azar, en forma de deriva genética, y no a la presión de selección.
Motoo Kimura postuló la Teoría Neutralista de la Evolución Molecular en 1983,[8] proponiendo que:
- La mayoría de las sustituciones de nucleótidos son el resultado de la fijación al azar de mutantes neutros, o casi neutros, más que el resultado de la selección natural
- Muchos de los polimorfismos proteicos son selectivamente neutros o casi neutros y su persistencia en la población se debe al equilibrio existente entre la aportación de polimorfismo por mutación y su eliminación al azar por deriva genética.
La teoría neutralista predice que para cada proteína o región génica existe una tasa constante de cambio por año, es decir que puede definirse un reloj molecular para cada región génica.
A menudo se ha contrapuesto la teoría neodarwinista (selección natural) al neutralismo (deriva genética). Sin embargo, ninguna de las dos teorías niega la acción tanto de la selección como de la deriva. La controversia radica en la importancia relativa que se otorga a una u otra fuerza evolutiva en la evolución molecular.[9]
Por otra parte, la teoría neutralista no postula que la morfología, la fisiología o el comportamiento evolucionan por deriva genética.
La teoría neutralista constituye la hipótesis nula de la evolución.
Coalescencia genealógica
El proceso de la deriva extendido en el tiempo lleva a la teoría de la coalescencia. La teoría de la coalescencia genética definida por Kingman en 1982[10] examina las relaciones genealógicas entre los genes. Según esta teoría, todos los genes (alelos) de un locus presentes en una población actual proceden de una única copia de ese gen en el pasado. En consecuencia, se pueden trazar los ascendientes de las copias génicas actuales hasta una sola copia génica ancestral.
La razón está en que en las poblaciones finitas todas las genealogías génicas menos una llegan a extinguirse con el tiempo.
Referencias
- ↑ Fontdevila, Antonio y Andrés Moya. 2000. Introducción a la Genética de Poblaciones. 349 p. Editorial Síntesis. ISBN: 84-7738-691-9
- ↑ Principios generales de la preservación de los recursos genéticos http://www.fao.org/docrep/005/ad013s/AD013S03.htm
- ↑ Mayr, Ernst. 1963. Animal Species and Evolution. 795 págs. Belknap Press of Harvard University Press. ISBN 0-674-03750-2
- ↑ Yashon, Ronnee K. y Michael R. Cummings. 2010. Genética humana y sociedad. 299 págs. Cengage Learning Eds. ISBN: 10-607-481-234-9.
- ↑ Rossi, María Susana y Luciano Levin. 2010. Qué es (y qué no es la evolución); el círculo de Darwin. 136 p. Siglo Veintiuno Editores. ISBN 978-987-1220-52-6.
- ↑ Hoelzel, A. R.; Halley, J.; O'Brien, S. J.; Campagna, C., Arnborm, T.; Le Boeuf, B. ; Ralls, K y G. A. Dover 1993. Elephant Seal Genetic Variation and the Use of Simulation Models to Investigate Historical Population Bottlenecks Journal of Heredity 84: 443-449 Online ISSN 1465-7333
- ↑ Curtis, Helena; Schneck, Adriana; Barnes, N. Sue y , Alicia Massarini. 2008. Biología. 1160 p. Ed. Médica Panamericana. . ISBN: 950-06-0334-8.
- ↑ Kimura, Motoo. 1983. The neutral theory of molecular evolution, Cambridge University Press, Cambridge (UK) ISBN 978-0-521-31793-1
- ↑ Orengo Ferriz, Dorcas J. 2011. Fundamentos de Biología molecular. 246 p. Editorial UOC. ISBN 978.84-9029-919-7
- ↑ Kingman, J.F.C. 1982. The coalescent. Stochastic Processes and Applications 13 :235-248 ISSN 03044149
Fuentes
- Campbell, Neil A.; Reece, Jane B.; Molles, Manuel; Urry, Lisa y Robin Heyden. 2007. Biología. 1392 p. Editorial Panamericana. ISBN 978-84-7963-998-1
- Curtis, Helena; Schneck, Adriana; Barnes, N. Sue y Alicia Massarini. 2008. Biología. 1160 p. Ed. Médica Panamericana. . ISBN: 950-06-0334-8
- Fontdevila, Antonio y Andrés Moya. 2000. Introducción a la Genética de Poblaciones. 349 p. Editorial Síntesis. ISBN: 84-7738-691-9