Traducción del ADN
| ||||||
Traducción del ácido desoxirribonucléico. La traducción es el proceso mediante el cual se produce la síntesis de proteínas. Este proceso ocurre en el citoplasma de la célula y para la mayoría de las proteínas de forma continua, durante todo el ciclo celular a excepción de la etapa M. Las funciones de las células siempre van a estar implicadas con las funciones de las proteínas por lo que la expresión de la información
genética como proteínas garantiza que las enzimas aceleren las reacciones del metabolismo, los transportadores posibiliten el intercambio de sustancias, los anticuerpos la defensa del organismo, las hormonas proteicas la regulación del metabolismo, los receptores el intercambio de información entre las células, entre otras.
Sumario
Localización subcelular
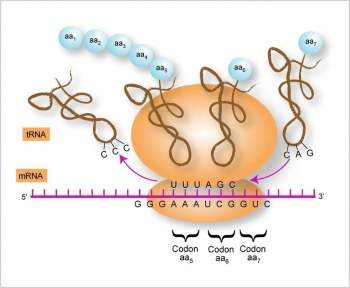
Como localización subcelular de la traducción se pude enunciar a los ribosomas. Organelos citoplasmáticos no membranosos, integrados por ARNr y proteínas. Los presentes en eucariontes tienen un coeficiente de flotación de 80s, con una subunidad mayor 60s y una menor 40s. La subunidad mayor presenta los ARN ribosomales: 5s, 5.8s y 28s; a los que se unen aproximadamente 50 tipos diferentes de proteínas. La subunidad menor presenta un solo ARN ribosomal: 18s, al que se unen 30 tipos diferentes de proteínas. Destacándose en ellos la presencia de tres sitios funcionales importantes:
- Sitio A: sitio por donde entran los ARNt con el aminoácido correspondiente al ribosoma.
- Sitio P: este es el lugar que ocupa el peptidil-ARNt; tan pronto el ARNt ceda su porción peptidil a la formación del nuevo enlace, pasará al siguiente sitio.
- Sitio E: corresponde al sitio ocupado por el ARNt sin el aminoacil ni el peptidil antes de abandonar el ribosoma. Es el sitio de salida de los ARNt descargados.
Características generales
Se caracteriza por ser un proceso gradual y repetitivo, lo que puede ser explicado de la siguiente manera: los aminoácidos son añadidos uno a uno por el mismo mecanismo. La síntesis se realiza de manera unidireccional pues ocurre siempre en dirección N-terminal a C-terminal. Se realiza de forma colineal a la lectura del ARNm, o sea que la síntesis de la cadena polipeptídica se realiza en la dirección N-terminal a C.terminal, mientras que la lectura del ARNm es en dirección 5'-3'. Por último el proceso está acoplado a la hidrólisis del GTP: la mayor parte de la energía requerida para el proceso se obtiene de la hidrólisis de este nucleótido.
Requerimientos
- Es necesario el ARNm que contiene la información de la proteína que se va a sintetizar.
- La presencia de determinados aminoácidos.
- La participación de ARNt que transfiera los aminoácidos al ribosoma.
- Proteínas enzimáticas y no enzimáticas, denominadas factores de traducción.
- Ribonucleósidos trifosfatados como fuente de energía.
Etapas fundamentales
Los especialistas a la hora de estudiar este proceso han elaborado un esquema que contiene cinco etapas básicas, caracterizadas por un conjunto de sucesos y transformaciones únicas para cada una de ellas.
Etapa de Preiniciación
Ocure la activación de los aminoácidos. Esta etapa ocurre en el citoplasma y consiste en la unión de cada aminoácidos a su ARNt específico. Esta reacción es catalizada por la enzima aminoacil-ARNt sintetasa. Cada uno de los veinte aminoácidos es reconocido por una aminoacil-ARNt sintetasa específica que pueden presentar de una a cuatro subunidades proteícas. La actividad de ellas es crítica para la exactitud posteriror de la traducción pues en el ribosoma ocurre un reconocimiento molecular entre las secuencias del codón y el anticodón, la frecuencia de errores en esta reacción es de 1 en 10000.
Etapa de Iniciación
El codón de iniciación (AUG) es identificado por el ribosoma con la ayuda de múltiples factores de iniciación (eIF). El codón AUG tiene una doble función: como iniciador, al costituir la señal para el primer aminoacil-ARNt, que es el metionil-ARNt iniciador, y como codón para la incorporación de metionina en el interior de la cadena polipeptídica que crecerá guiada por el ARNm y que corresponde con la etapa de elongación. La etapa de iniciación ha sido dividida en varias subetapas las que culminan con un ribosoma listo a incorporar al siguiente aminoácido en el sitio A para dar lugar a la siguiente etapa. Primero ocurre la disociación del ribosoma en sus dos subunidades, lo que es asistido por varios factores de iniciación. Luego se forma el complejo ternario eIF-2-GTP-Met-ARNtiMet, donde el eIF-2 es una proteína que une al GTP y reconoce al ARNt iniciador (Met-ARNtiMet). Finalmente sucede la unión del complejo ternario a la subunidad menor del ribosoma (40s). Le sigue el reconocimiento del casquete del extremo 5' del ARNm por el factor de iniciación eIF-4F e incorporación a la subunidad menor. Como penúltima subetapa se encuentra el movimiento de la subunidad menor unida al ARNm a lo largo del extremo 5', proceso que se denomina scanning y que require energía y factores de iniciación adicionales. Por último, en el momento en que la subunidad menor activada alcanza la posición del codón AUG, la subunidad mayor se une a la menor.
Etapa de Elongación
En esta etapa ocurre la formación del enlace polimerizante durante la formación de la proteína. Aquí, al igual que en las otras etapas, la participación de proteínas adicionales no ribosómicas es fundamental; las que se denominan factores de elongación (eEF). También se divide en fases:
- Los aminoácidpos activados se unen a un factor de elongación en presencia de GTP. La entrada de cada ARNt al sitio A del ribosoma con un consiguiente gasto de energía (GTP).
- El complejo entra al sitio A regido por la complementariedad codón-anticodón por lo que se require de una prueba de lectura del codón. Si ocurriera una entrada incorrecta este sería expulsada del sitio para entrar al aa-ARNt correcto.
- Cuando los ARNt están correctamente situados ocurre la formación del enlace peptídico con la acción de la peptidil transferasa.
- En esta fase se localiza el codón que ocupará el sitio A para que pueda entrar el
aminoacil-ARNt a dicho sitio. Esto requiere un movimiento del ribosoma denominado traslocación y que ocurre simultáneamente con la salida del aminoacil-ARNt descargado. Un factor de elongación (eEF-2) y la energía del GTP son utilizados en esta fase.
- Los eventos anteriores se repiten hasta que al sitio A llegue un codón de terminación, que no codifica aminoácido alguno.
Etapa de Terminación
Como los codones de terminación no tienen ARNt que los identifique, en su lugar esto constituye una señal para dar inicio a la terminación de la traducción. El codón de terminación es reconocido por un factor de liberación unido al GTP. Dicho complejo se une al ribosoma en el sitio A y con la hidrólisis del GTP se produce la liberación de la cadena polipeptídica sintetizada y el desensamblaje de la maquinaria sintetizadora. En estos momentos el ribosoma se encuentra en condiciones de iniciar un nuevo evento de traducción.
Etapa de Posterminación
Esta etapa corresponde a la maduración o procesamiento de la molécula formada. Durante esta etapa la proteína alcanza su estructura y conformación con su actividad biológica. Existen diversos eventos que posibilitan que la proteína logre su estado funcional, entre ellos se encuentran: la eliminación de aminoácidos de los extremos y del interior de la cadena; la transformación de los aminoácidos en reacciones de hidrolización, obteniéndose hidroxiprolina y hidroxilisina, aminoácidos que aparecen en el colágeno; incorporación de grupos prostéticos, incorporación de metales en las metaloproteínas, formación de enlaces disulfuro, glicosilaciones y el ensamblaje de subunidades en las proteínas oligoméricas.
Inhibidores de la transcripción
Existen algunos antibióticos que interfieren en el proceso de traducción. Se aprovechan de las diferencias entre los mecanismos de traducción procarióta y eucarióta para inhibir selectivamente la síntesis de proteínas en las bacterias sin afectar al huésped. Entre ellos se pueden destacar:
- La puromicina que tiene una estructura similar al aminoacil-ARNt de la tirosina. Por tanto, se enlaza al sitio A del ribosoma y participa en la formación de enlaces peptídicos, produciendo peptidil-puromicina. Sin embargo, no toma parte en la traslación y se desacopla rápidamente del ribosoma, causando una terminación prematura de la síntesis del polipéptido.
- La streptomicina provoca una mala lectura del código genético en las bacterias a concentraciones relativamente bajas e inhibe la iniciación a concentraciones mayores, enlazándose a la subunidad ribosómica 30s.
- Aminoglucósidos como la tobramicina y la kanamicina evitan la asociación ribosómica al final de la fase de iniciación y provocan una mala lectura del código genético.
- Las tetraciclinas bloquean el sitio A del ribosoma, evitando el acoplamiento de los aminoacil-ARNt.
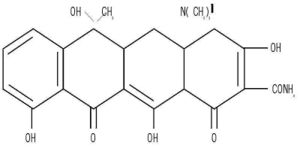
- El cloranfenicol bloquea la fase de la transferencia peptídica de la elongación en la subunidad ribosómica 50s, tanto en las bacterias como en las mitocondrias.
- Losmacrólidos y las lincosamidas se enlazan a las subunidades ribosómicas 50s, inhibiendo la reacción de la peptidiltransferasa o la traslación, o ambas cosas.
Véase también
Enlaces externos
- El misterioso elfo de Leewenhoek: el recorrido desde el microscopio hasta el ADN en el Museu Virtual Interactivo de la Genética y el ADN
- Modelo en 3 dimensiones de la estructura del ADN. Interactivo. Requiere Java.
- Instituto de Genética Humana
Fuentes
- Colectivo de autores. Morfofisiología Humana I. Editorial: Ecimed, La Habana, 2007. ISBN 978-959-212-244-4
- De Robertis EDP, De Robertis EMF. Biología Celular y Molecular. Editorial: Revolucionaria, La Habana, 1984.
- Cardellá-Hernández y otros autores. Bioquímica Médica II. Editorial: Ecimed, La Habana, 1999. ISBN 959-7132-16-8
- Diccionario Terminológico de Ciencias médicas. Editorial: Revolucionaria, La Habana, 1984.